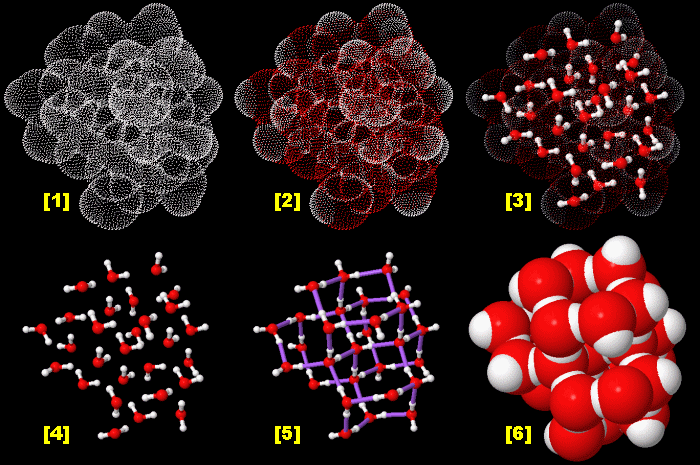
- METTL18-mediated histidine methylation of RPL3 modulates translation elongation for proteostasis maintenance(eLife,2022/06/20)
- DNAとRNAのいろいろな姿(本サイト) | コドンと遺伝暗号表
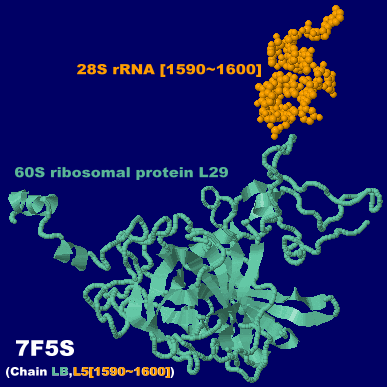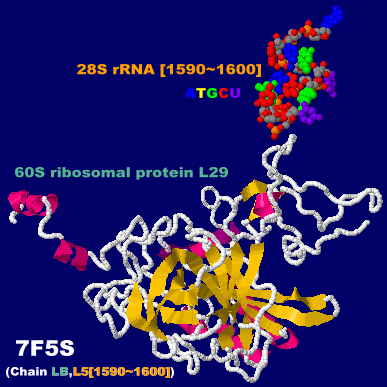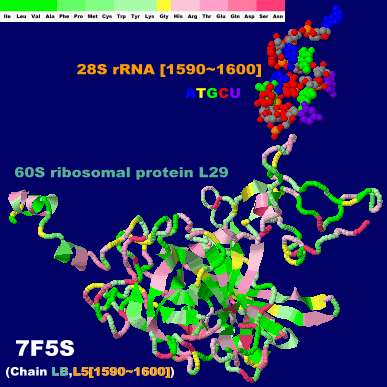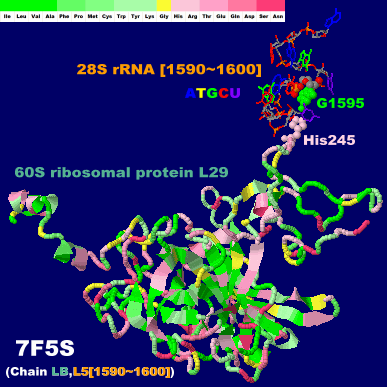
リボソームタンパク質とmRNAの複合体7f5sChain LB・L5(塩基番号1590〜1600のみ);His245・G1595については理研プレスリリース図2参照
-
●アミノ色表示の凡例
ASP GLU CYS MET LYS ARG SER THR PHE TYR ASN GLN GLY LEU VAL ILE ALA TRP HIS PRO
●酸性・中性〈芳香族〉・塩基性アミノ酸区別表示の凡例
ASP GLU GLY ALA VAL LEU ILE CYS SER THR ASN GLN PRO MET PHE TYR TRP LYS ARG HIS
●極性〈酸性・塩基性〉・非極性(疎水性)アミノ酸区別
SER THR TYR CYS ASN GLN ASP GLU LYS ARG HIS GLY ALA VAL LEU ILE PHE PRO MET TRP
●疎水性インデックス順
ARG LYS ASN ASP GLN GLU HIS PRO TYR TRP SER THR GLY ALA MET CYS PHE LEU VAL ILE
●有機概念図I/O値順(特性基 R)
ASN SER ASP GLN GLU THR ARG HIS GLY LYS TYR TRP CYS MET PRO PHE ALA VAL LEU ILE
●等電点順
ASP GLU CYS ASN PHE GLN TYR SER MET TRP VAL GLY LEU ALA ILE THR PRO HIS LYS ARG
アミノ酸および特性基の親水性・疎水性 | Log Pをポケットに!
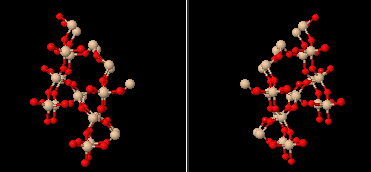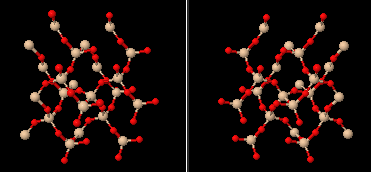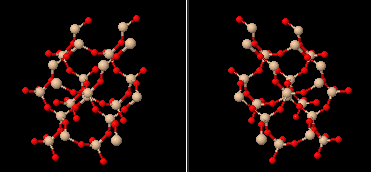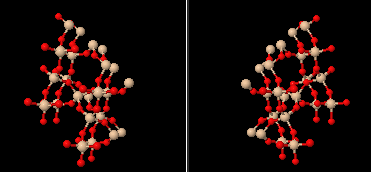
塩化ナトリウムの結晶構造
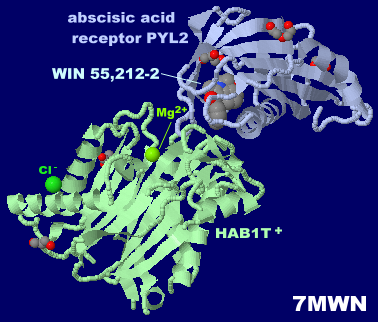
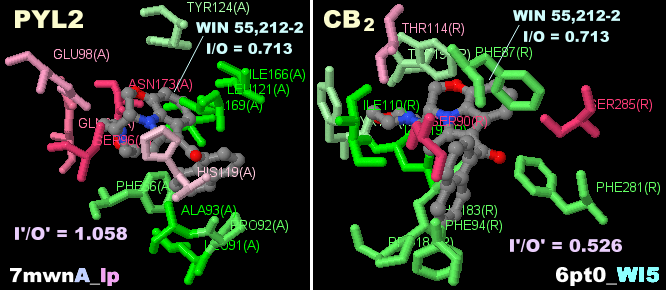
WIN 55,212-2が結合した植物ホルモン受容体7mwnとそのPDBsumデータ(別研究の6pt0との比較 → GPCR)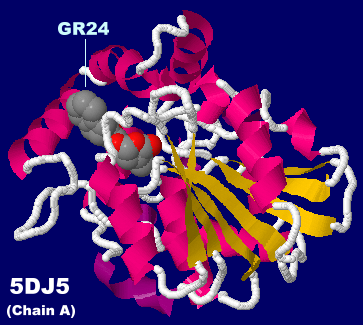
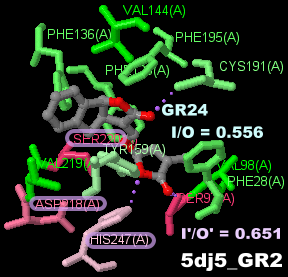
ストリゴラクトンGR24が結合した植物ホルモン受容体DWARF14 5dj5のChain A
[Excitatory amino acid transporter 2 - Wikipedia,WAY-213,613 - Wikipedia]
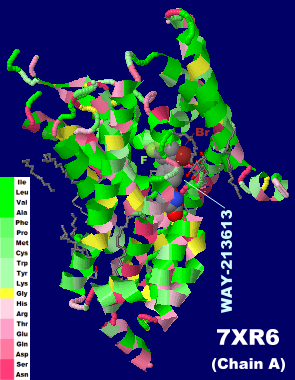
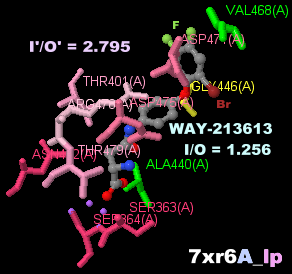
WAY-213613が結合したグルタミン酸トランスポーター2(EAAT2)7xr6のChain AとそのPDBsumデータ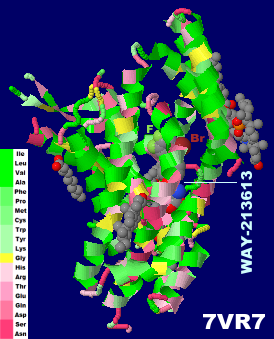
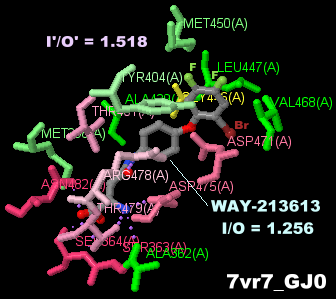
同7vr7とそのPDBsumデータ
[DNA repair - Wikipedia]
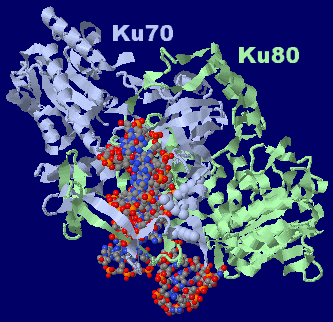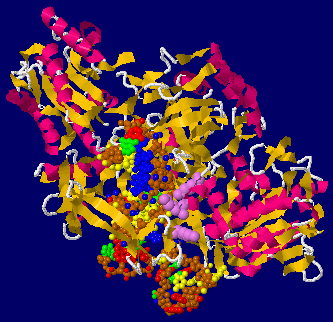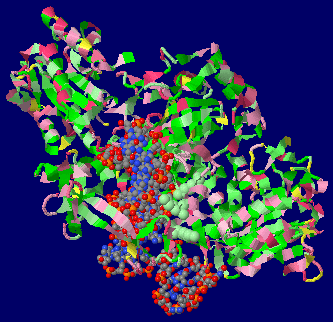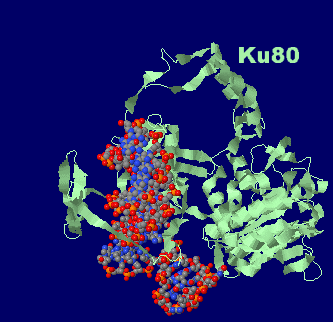
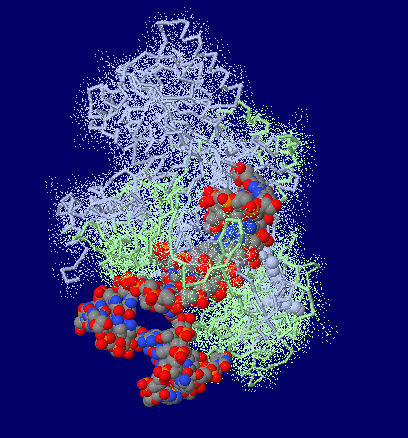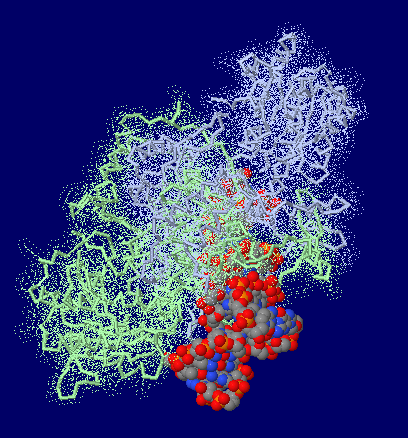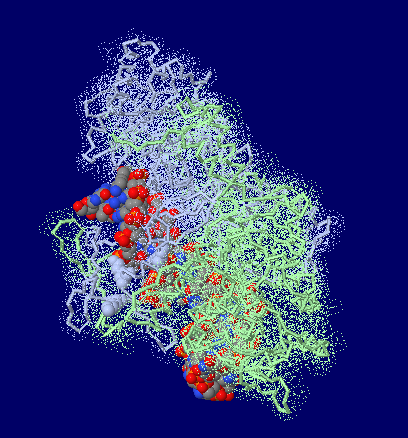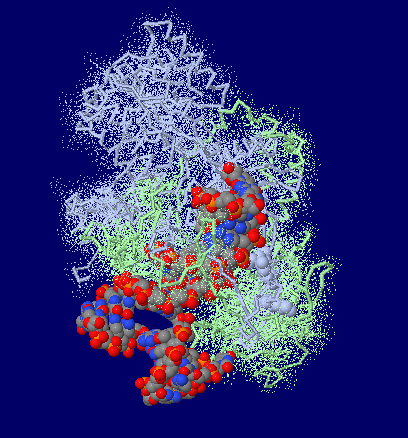
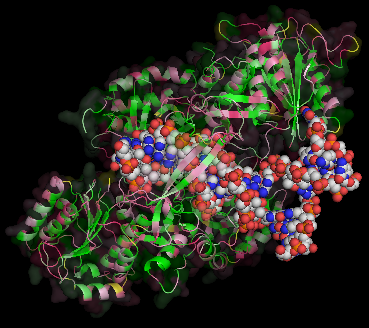
Kuタンパク質(2本鎖切断DNA修復タンパク質;Ku70,Ku80)/DNA複合体1jey;右はPyMOLによる表示例
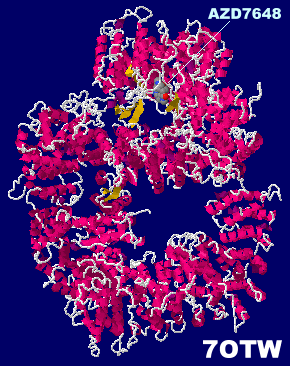
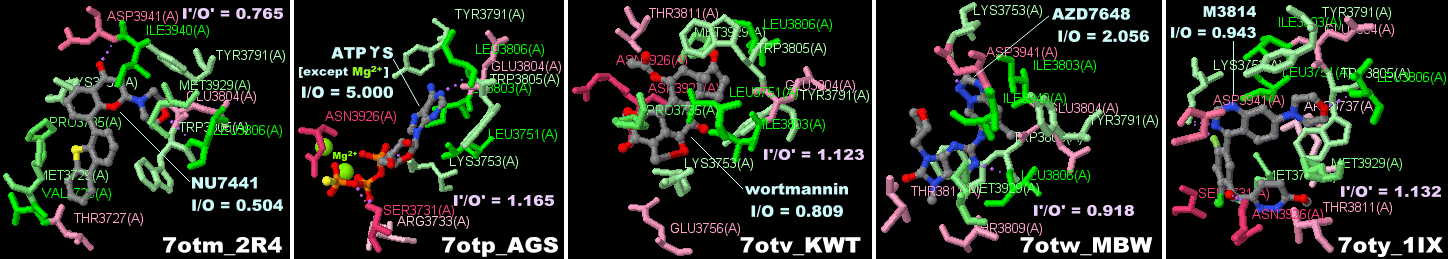
AZD7648が結合したDNA依存性プロテインキナーゼ触媒サブユニットDNA-PKcs 7otwとそのPDBsumデータ(リガンドがそれぞれNU7441・ATPγS・wortmannin・M3814のデータとの比較)
[ABC transporter - Wikipedia]
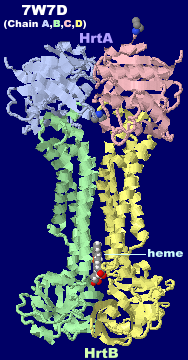
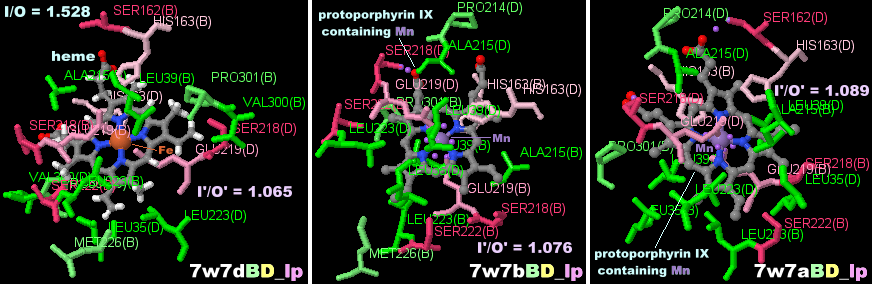
ヘムが結合したABCトランスポーターHrtBA 7w7dのChain A-DとそのPDBsumデータ(7w7b・7w7aとの比較)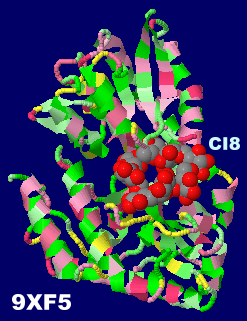
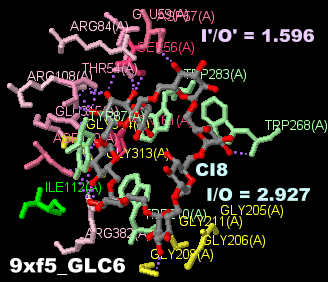
グルコース8量体CI8が結合したABCトランスポーター9xf5とPDBsumデータ
 ★同書新版裏表紙の「北海道石」を日本コンピュータ化学会@サイエンスアゴラ2023(テレコムセンタービル,11/18-19)でブース展示し,11/19の13:00-15:00には発見メンバーの田中陵二さんに解説していただきました。
★同書新版裏表紙の「北海道石」を日本コンピュータ化学会@サイエンスアゴラ2023(テレコムセンタービル,11/18-19)でブース展示し,11/19の13:00-15:00には発見メンバーの田中陵二さんに解説していただきました。
★田中陵二さんをゲストにお迎えして第118回サイエンスカフェにいがた『ふしぎな新鉱物「北海道石」を知ろう! 楽しもう!』(2024/04/22)を開催し,「北海道石」実物をご覧いただきました。


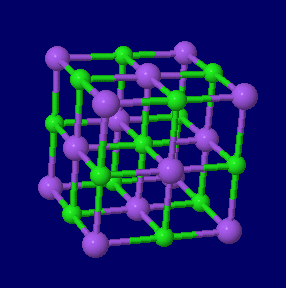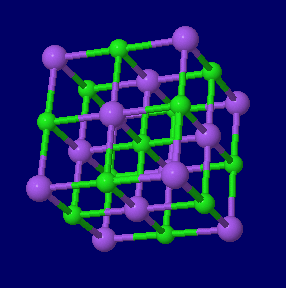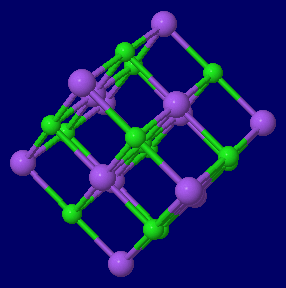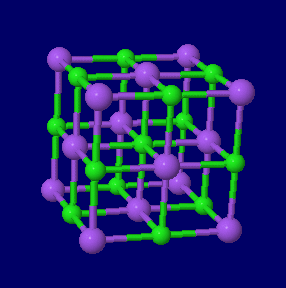
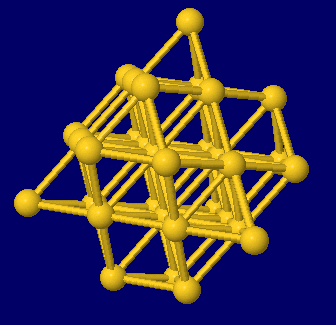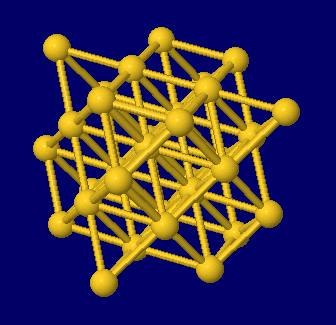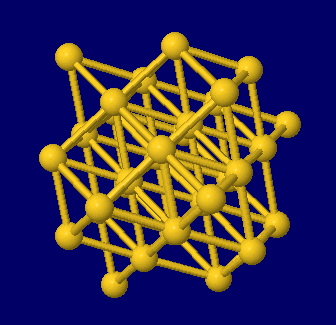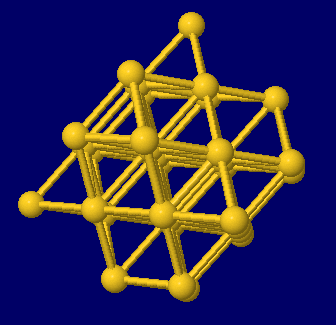

左から 塩化ナトリウム(NaCl),金(Au),金・銀・銅の結晶構造同時表示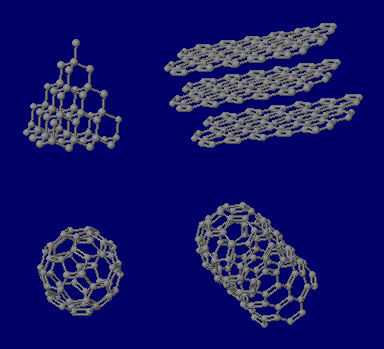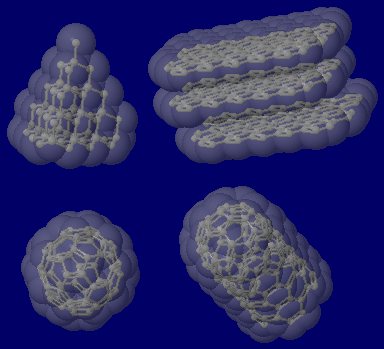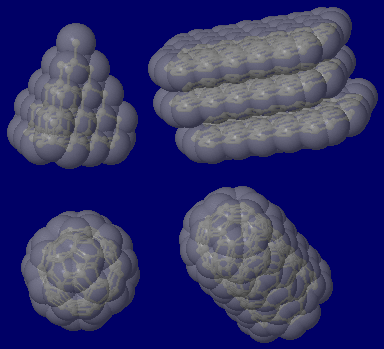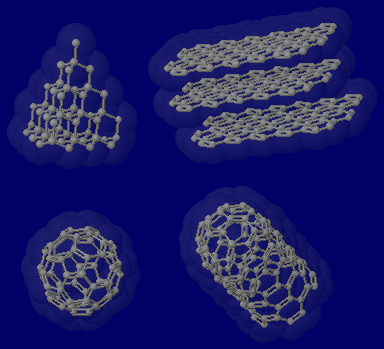
炭素(C)の同素体の例(ダイヤモンド,グラファイト,フラーレン,カーボンナノチューブの部分構造例)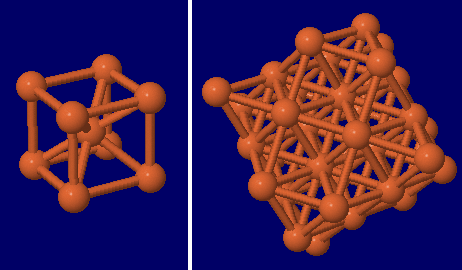
鉄(Fe)の体心立方格子と面心立方格子構造の結晶)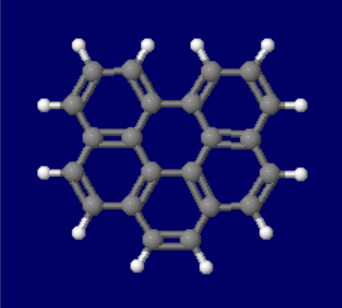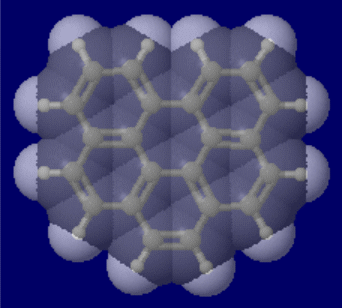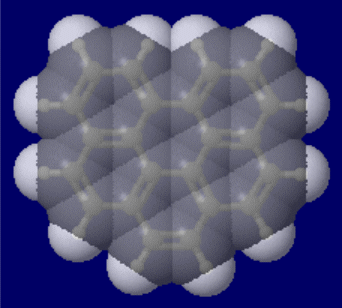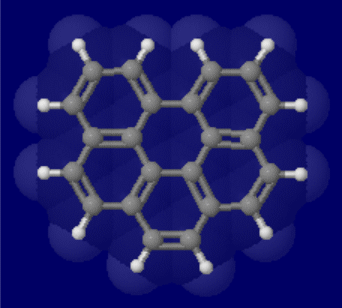

[左]ベンゾ[ghi]ペリレン(benzo[ghi]perylene) [右]同分子とコロネン(coronene)の同時表示(●は炭素)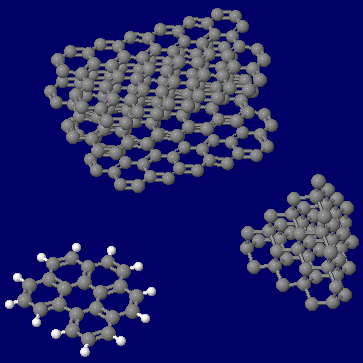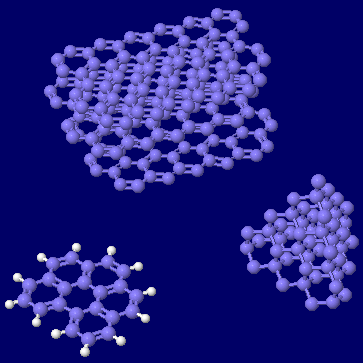

ベンゾ[ghi]ペリレンとダイヤモンドとグラファイトの同時表示(アニメgifで●は炭素)およびその3Dプリンタ模型(スタジオミダス製作)


左から 日本コンピュータ化学会@サイエンスアゴラ2023での北海道石展示(上掲書著者の田中さんのご協力による),
同解説パネル,ベンゾ[ghi]ペリレン・コロネン・ピセンを含む展示鉱石
※日本コンピュータ化学会2023秋季年会一般公開イベント(2023/11/26,高松市 レクザムホール)でも展示させていただきました。 → 会場写真
[Auxin - Wikipedia,PIN proteins - Wikipedia]
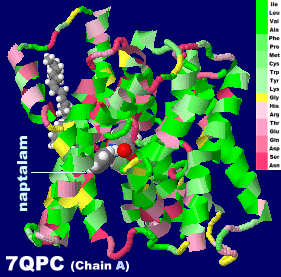
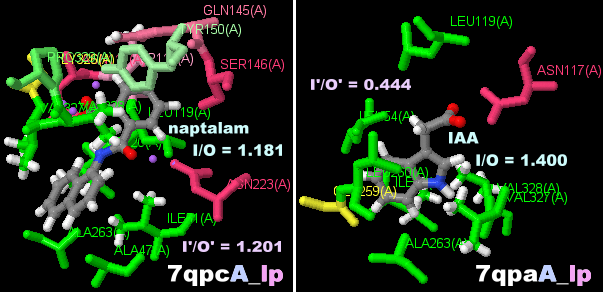
[左・中]ナプタラム(naptalam)が結合したオーキシントランスポーター7qpcのChain AとそのPDBsumデータ(インドール-3-酢酸結合の7qpaとの比較)
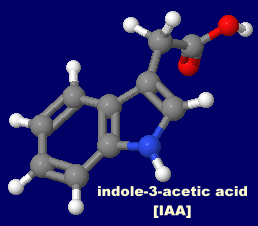
[右]植物ホルモンのオーキシンの例インドール-3-酢酸(indole-3-acetic acid;IAA)
[Serine hydroxymethyltransferase - Wikipedia]
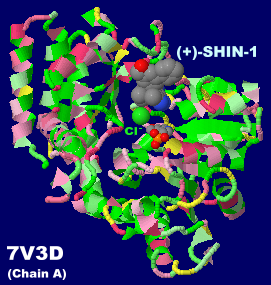
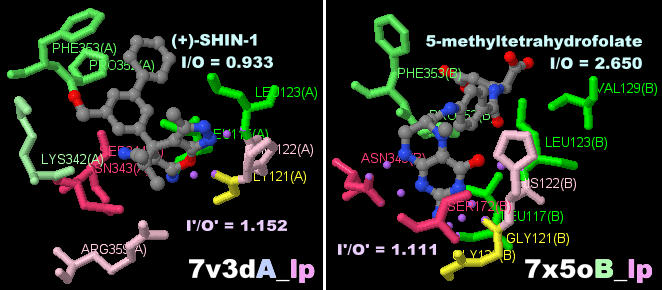
(+)-SHIN-1が結合したセリンヒドロキシメチルトランスフェラーゼ(SHMT)7v3dのChain AとそのPDBsumデータ(5-メチルテトラヒドロ葉酸結合の7x5oとの比較)
[Nitric oxide synthase - Wikipedia]
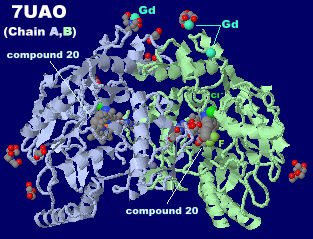
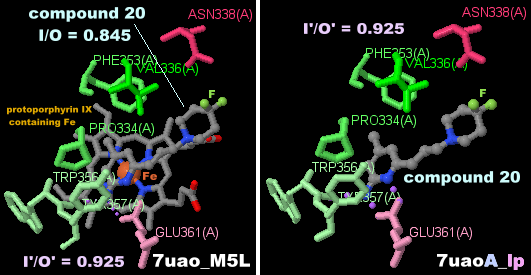
一酸化窒素合成酵素7uaoのChain A・BとそのPDBsumデータ(LigPlot+によるものとの比較;I'/O'値は同じ)
[Glucose-6-phosphate dehydrogenase - Wikipedia]
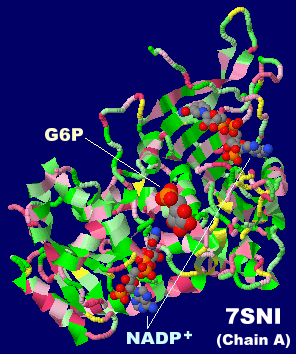
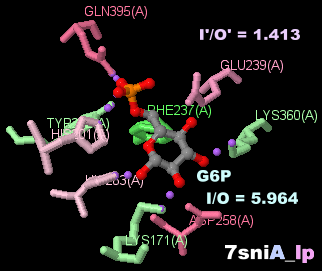
β-D-グルコース-6-リン酸(G6P)とNADP+が結合したグルコース-6-リン酸デヒドロゲナーゼ7sniのChain AとG6PのPDBsumデータ