- Structural insights into inhibition mechanism of the helicase-primase complex from human herpesvirus 1(Cell Chemical Biology,2026/04/15) [NEW!] ※2026/04/08公開9ut1(下掲)・9ut3・9ut4・9ut5・9ut6・9ut7
- 【横浜市立大学】抗ヘルペスウイルス薬が働く仕組みを原子レベルで解明(紀伊民報,2026/04/16) [NEW!]
[Amenamevir - Wikipedia]
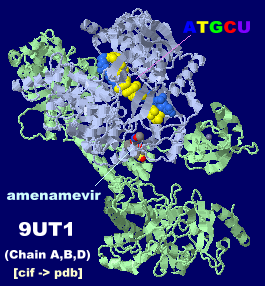
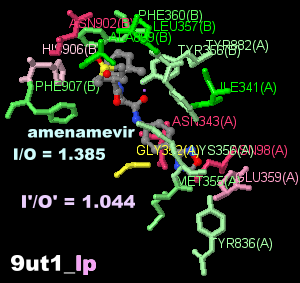
DNAとアメナメビル(amenamevir)が結合した単純ヘルペスウイルス由来HPC(ヘリケース・プライメース複合体)の構造9ut1のChain A・B・DとPDBsumデータ
-
●アミノ色表示の凡例
ASP GLU CYS MET LYS ARG SER THR PHE TYR ASN GLN GLY LEU VAL ILE ALA TRP HIS PRO
●酸性・中性〈芳香族〉・塩基性アミノ酸区別表示の凡例
ASP GLU GLY ALA VAL LEU ILE CYS SER THR ASN GLN PRO MET PHE TYR TRP LYS ARG HIS
●極性〈酸性・塩基性〉・非極性(疎水性)アミノ酸区別
SER THR TYR CYS ASN GLN ASP GLU LYS ARG HIS GLY ALA VAL LEU ILE PHE PRO MET TRP
●疎水性インデックス順
ARG LYS ASN ASP GLN GLU HIS PRO TYR TRP SER THR GLY ALA MET CYS PHE LEU VAL ILE
●有機概念図I/O値順(特性基 R)
ASN SER ASP GLN GLU THR ARG HIS GLY LYS TYR TRP CYS MET PRO PHE ALA VAL LEU ILE
●等電点順
ASP GLU CYS ASN PHE GLN TYR SER MET TRP VAL GLY LEU ALA ILE THR PRO HIS LYS ARG
●ヒトの必須・非必須区別
ILE LEU VAL PHE MET TRP LYS HIS THR ARG ALA PRO CYS TYR GLY GLU GLN ASP SER ASN
アミノ酸および特性基の親水性・疎水性 | Log Pをポケットに!